Zellfreie Suche nach neuen Antibiotika durch Kopplung von Synthetischer Biologie mit KI
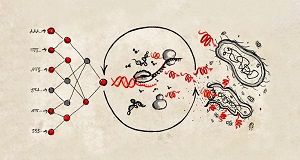
Die zunehmende Resistenz von Bakterien gegen Antibiotika stellt eine
wachsende globale Gesundheitsbedrohung dar. Forschende des Max-Planck-
Instituts für terrestrische Mikrobiologie in Marburg entwickelten nun mit
Hilfe der Synthetischen Biologie und Künstlicher Intelligenz (KI) einen
effizienteren Ansatz zur Entdeckung und Herstellung neuer antimikrobieller
Peptide, die gegen ein breites Spektrum von Bakterien wirken können.
Bioaktive Peptide spielen eine Schlüsselrolle in Gesundheit und Medizin.
Derzeit sind mehr als 80 peptidbasierte Medikamente im Einsatz, die alle
aus natürlichen Quellen isoliert wurden. Es wird jedoch geschätzt, dass
Antibiotikaresistenzen jedes Jahr weltweit mehr als eine Million
Todesfälle verursachen. Es wird erwartet, dass diese Zahl bis 2050 auf 10
Millionen ansteigen wird, so dass dringend neue Methoden benötigt werden,
um die Entwicklung neuer antimikrobieller Wirkstoffe zu beschleunigen. Ein
ungenutztes Potenzial liegt im nicht-natürlichen Bereich, wo
schätzungsweise eine Anzahl von 20 hoch 10 bis zu 20 hoch 30 verschiedene
Peptide noch unerschlossen sind.
In Zusammenarbeit mit mehreren Labors am MPI für terrestrische
Mikrobiologie, der Universität Marburg, dem MPI für Biophysik, dem
Institut für Mikrobiologie der Bundeswehr, dem iLung Institut und INRAe
Frankreich hat ein Team von Wissenschaftlern des Max-Planck-Instituts
unter der Leitung von Prof. Tobias Erb eine neue Pipeline für die
Entwicklung bioaktiver Peptide entwickelt.
"Beim Deep Learning lernt ein neuronales Netzwerk mit Algorithmen, die
durch das menschliche Gehirn inspiriert sind, aus großen Datenmengen.
Diese Art des maschinellen Lernens ist für die Entdeckung von Peptiden und
für das De-novo-Design sehr vielversprechend. In der Regel folgt darauf
jedoch die chemische Herstellung von Peptiden für experimentelle Tests,
was recht schwierig und zeitaufwändig ist. Die Zahl der Peptide, die
chemisch hergestellt werden können, ist daher sehr begrenzt", erklärt Amir
Pandi, Doctoral Student in der Arbeitsgruppe von Prof. Dr. Tobias Erb und
Erstautor der Studie.
Um diese Einschränkungen zu überwinden, entwickelte das Forscherteam eine
zellfreie Proteinsynthese (CFPS) für die schnelle und kostengünstige
Herstellung von antimikrobiellen Peptiden (AMPs) direkt aus DNA-Templates.
Das neue Protokoll bietet eine effiziente und kostengünstige
Hochdurchsatzmethode für das AMP-Screening.
Das Team verwendete zunächst sogenanntes generatives Deep Learning, um
Tausende von AMPs de novo zu entwerfen, und anschließend prädiktives Deep
Learning, um diese auf 500 Kandidaten einzugrenzen. Von diesen Kandidaten
wurden durch das Screening mit der zellfreien Pipeline 30 funktionelle
AMPs identifiziert, die die Forscher durch Molekulardynamiksimulationen
und die Bestimmung ihrer antimikrobiellen Aktivität und Toxizität weiter
charakterisierten.
Bemerkenswerterweise zeigten sechs der AMPs ein breites Wirkungsspektrum
gegen multiresistente Erreger und es kam zu keiner bakteriellen
Resistenzentwicklung.
"Wir haben von der Kombination aus zellfreier synthetischer Biologie,
künstlicher Intelligenz und Hochdurchsatzverfahren sehr profitiert. Indem
wir die Anzahl der Kandidaten erhöhen, die in weniger als 24 Stunden
experimentell getestet werden können, steigt die Chance, aktive AMPs zu
finden", sagt Amir Pandi. "Unsere CFPS-Pipeline ergänzt nicht nur die
jüngsten Fortschritte im computergestützten Wirkstoffdesign. Sie hat auch
das Potenzial, die Beziehung zwischen Design und Funktion bioaktiver
Peptide schneller und kostengünstiger zu erforschen". Tobias Erb fügt
hinzu: "Diese neue Methode an der Schnittstelle von synthetischer Biologie
und maschinellem Lernen wird für Wissenschaftlerinnen und Wissenschaftler
interessant sein, die in den Bereichen Biomedizin und bioaktiven
Peptidengineering arbeiten."
Zu den nächsten Schritten gehören die weitere Verbesserung der Ausbeute
bei der Peptidproduktion sowie der Einsatz von KI und Ansätzen der
synthetischen Biologie, um neue AMPs zu entwickeln, die stabiler und
weniger toxisch sind oder eine spezifische Wirkungsweise haben. Die
Forscher planen auch den Einsatz erweiterter generativer KI-Modelle. Dabei
lernt die Maschine molekulare Repräsentationen für gewünschte
Eigenschaften, was die Erfolgsquote bei der Identifizierung von
Wirkstoffkandidaten erhöhen würde.





